栽培ギクの起源を明らかにし、品種改良を加速
2019-02-04 農研機構
かずさDNA研究所、農研機構、東京大学、広島大学および日本大学は共同で、キクタニギクのゲノム解析を行い、開花に関わる遺伝子の探索と栽培ギクのゲノム配列変異の検出などを行いました。
キクタニギクはキク科キク属の植物で、日本では東北から九州にかけて自生しています。栽培ギクに比べてゲノム構造が単純なため、キクのモデル植物としてさまざまな研究に利用されています。
今回、全ゲノムの89%にあたる2.72Gbの配列を解読しました。解読した配列から推定された遺伝子数は71,057です。
キクタニギクのゲノムや開花に関わる遺伝子が明らかになったことで、キクの開花制御や花の形態形成に関する研究を一層すすめることができます。そして、これらの情報を利用した栽培ギクの育種の効率化が進むと期待できます。
研究成果は、DNA Research誌で1月27日にオンライン公開されました。
論文タイトル:De novo whole-genome assembly in Chrysanthemum seticuspe, a model species of Chrysanthemums, and its application to genetic and gene discovery analysis.(キク属のモデル種であるキクタニギクにおける全ゲノム構築とその遺伝学および遺伝子発掘解析への応用)
論文のURL: https://academic.oup.com/dnaresearch/advance-article/doi/10.1093/dnares/dsy048/5303208
DOI:10.1093/dnares/dsy048
データベース:MumGARDEN (http://mum-garden.kazusa.or.jp/)
NBRP広義キク属:http://shigen.nig.ac.jp/chrysanthemum/index.jsp

キクタニギクの写真:広島大学提供
詳しいプレスリリース
〜栽培ギクの起源を明らかにし、品種改良を加速〜
1 月27日に DNA Research でオンライン発表
平成31年2月4日
公益財団法人 かずさDNA研究所
国立研究開発法人 農業・食品産業技術総合研究機構(農研機構)
国立大学法人 東京大学
国立大学法人広島大学
学校法人 日本大学
◇かずさDNA研究所、農研機構、東京大学、広島大学および日本大学は共同で、キクタニギ クのゲノム解析を行い、開花に関わる遺伝子の探索と栽培ギクのゲノム配列変異の検出など を行いました。
◇ キクタニギクはキク科キク属の植物で、日本では東北から九州にかけて自生しています。栽 培ギクに比べてゲノム構造が単純なため、キクのモデル植物としてさまざまな研究に利用さ れています。
◇ 今回、全ゲノムの 89%にあたる 2.72Gb の配列を解読しました。解読した配列から推定され た遺伝子数は 71,057 です。
◇ キクタニギクのゲノムや開花に関わる遺伝子が明らかになったことで、キクの開花制御や花 の形態形成に関する研究を一層すすめることができます。そして、これらの情報を利用した 栽培ギクの育種の効率化が進むと期待できます。
◇ 研究成果は、DNA Research 誌で1月27日にオンライン公開されました。(問い合わせ先)
<報道に関すること> 公益財団法人かずさDNA研究所 広報・研究推進グループ
<研究に関すること> 公益財団法人かずさDNA研究所 植物ゲノム・遺伝学研究室 室長 磯部 祥子(いそべ さちこ) 1. 背景
キク科に属する植物種は被子植物の約 10%を占め、特に栽培ギクの起源となったキク属は 主に東アジアで分化したことから、植物の多様性を研究する上で重要な植物群のひとつです。 また、栽培ギクは日本の切花生産の約 40%を占めており、世界的にもバラやカーネーション と並んで重要な花き品目です。
今回解析したキクタニギク(Chrysanthemum seticuspe)は、キク科キク属の多年草で、東 北から九州にかけて自生しており、10~11 月に黄色い花をつけます。キクタニギクの染色体 数は 2n=18 ですが、栽培されているキクは多くの野生ギクが交雑を繰り返し品種として成立 したため、複雑なゲノム構造になっています。そのため、ゲノム構造が単純なキクタニギク が、キクのモデル植物として開花制御の研究などに利用されています。
キク属の遺伝学的研究がこれまで進んでいなかった理由としては、自家不和合性もありま す。通常のキクタニギクは、同じ個体の花にある雄蕊(ゆうずい;おしべ)の花粉が雌蕊(し ずい;めしべ)についても種子がほとんどできません(他殖性、と言います)。そのため、遺 伝学的な研究に重要な、ゲノム構造が同質で安定した形質が現れる、いわゆる「純系」と呼ば れる系統をつくることができなかったのです。
広島大学は、同一個体の花粉で種子を作ることができる(自殖性)個体「AEV2」を発見し、 文部科学省・ナショナルバイオリースプログラムのもと、この「AEV2」を用いて 5 回の自殖を 繰り返しました。そして、ゲノム配列の構造がより同質化された系統「XMRS10」を作出し、ゲ ノム解析を行いました。
本研究では、広島大学で作出された「XMRS10」を用いて、かずさDNA研究所および農研機 構野菜花き研究部門でゲノム配列の解読と遺伝子予測、連鎖地図の作成を行いました。また、 農研機構野菜花き研究部門と東京大学、日本大学において生育・開花に関わる遺伝子の探索を 実施しました。キクタニギクのゲノムサイズの推定は農研機構野菜花き研究部門で、栽培キク ゲノムの配列変異の検出はかずさDNA研究所で行いました。
キクタニギクは、文部科学省・ナショナルバイオリソースプロジェクト(NBRP)広義キク属 で、バイオリソースとして扱われています。プロジェクトについては、HP をご覧ください。 NBRP 広義キク属:http://shigen.nig.ac.jp/chrysanthemum/index.jsp
2. 研究成果の概要と意義
① 超並列シークエンシング技術と大型計算機を駆使し、キクタニギクの全ゲノムの 89%に あたる 27 億 2000 万塩基対(2.72Gb)の配列を解読しました。
② 解読された配列から推定された遺伝子数は 71,057 でした。このうち開花に関わる遺伝子 として 221 の遺伝子がみいだされました。
③ ゲノム配列から開花関連の遺伝子を探索し、シロイヌナズナなどで花成抑制遺伝子とし て報告されている CEN 様遺伝子をあらたに見つけることができました。また、日長や温 3 度処理を変えたときのキクタニギク茎頂での遺伝子発現解析により、新たに見つかった 遺伝子は季節変動に応じて開花・休眠を制御する遺伝子である可能性が示唆されました。 ④ 解読したゲノム配列を用いて、自殖系統と他殖系統の個体群がそれぞれもつ、配列の変 異を染色体上に並べた連鎖地図を作成しました。
⑤ 解読したゲノムと栽培ギク 6 系統のゲノム配列を比較して、合計で 95 万 4706 の配列の 違い(1塩基多型、SNPs)を検出しました。このうち 533 の変異は、遺伝子機能の変異 に関わる可能性が極めて高い変異であると推定されました。
⑥ キクタニギクで推定された遺伝子配列を、同じキク科のヒマワリ、レタスの遺伝子配列 と比較したところ、キクタニギクはヒマワリとより近縁であり、およそ 4600 万年前にキ クタニギクとヒマワリが分岐したと推定できました。
⑦ 本研究により得られた情報は、データベースとして公開しています。 MumGARDEN (http://mum-garden.kazusa.or.jp/)
3. 将来の波及効果
① 世界で初めてキクタニギクのゲノム解読に成功したことで、栽培キクのモデル植物であ るキクタニギクや栽培ギクの遺伝子の解明などの研究を進めることができます。
② 栽培ギクではこれまでゲノム情報を用いた育種があまり実施されていませんでしたが、 キクタニギクのゲノム配列情報を用いることで、栽培ギクの有用形質を選抜するための ゲノム情報を得やすくなり、栽培ギクの育種が進むことが期待できます。
③ キクは古くから電照により開花を制御するなど、開花日を調節した栽培が実施されてき ました。キクタニギクで探索された開花に関する遺伝子配列の機能解析をすすめて、キ クの開花メカニズムを明らかにすることで、より精度の高いキクの栽培法の開発につな がることが期待できます。
この研究は、農林水産省・委託プロジェクト(園芸ニーズ・DHR5)、JSPS・科学研究費助成事業 基盤 B(No. 16H04877)、およびかずさ DNA 研究所の助成によって行われました。
論文タイトル:De novo whole-genome assembly in Chrysanthemum seticuspe, a model species of Chrysanthemums, and its application to genetic and gene discovery analysis.
著者:Hideki Hirakawa*, Katsuhiko Sumitomo*, Tamotsu Hisamatsu, Soichiro Nagano, Kenta Shirasawa, Yohei Higuchi, Makoto Kusaba, Masaji Koshioka, Yoshihiro Nakano, Masafumi Yagi, Hiroyasu Yamaguchi, Kenji Taniguchi, Michiharu Nakano and Sachiko N Isobe.
掲載誌:DNA Research
DOI:10.1093/dnares/dsy048
用語解説
*1 遺伝子:親から子へと遺伝する、あるいは細胞から細胞へと伝えられる形質を決定する因子で あり、生物の体を作り動かすのに必要なタンパク質などを作るための設計図のことで、その本体 は DNA である。
*2 ゲノム:生物をその生物たらしめるのに必須な最小限の染色体のひとまとまり、または DNA 全 体のことをいう。
参考となる図や写真
写真:キクタニギク(広島大学提供)

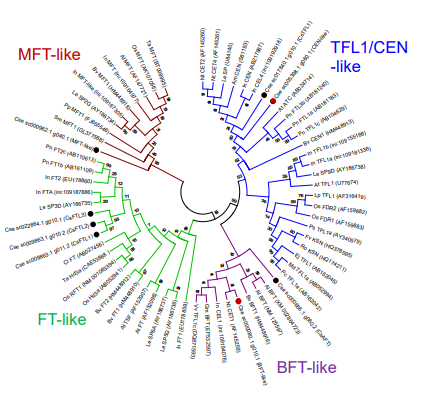
図1:探索した開花に関連する 遺伝子のうち、花成ホルモン (フロリゲン)を含む PEBP (phosphatidylethanolaminebinding protein) ファミリーに 属するに関連する遺伝子群と他 種で同定されている遺伝子との 配列の類似性を示した系統樹。 黒丸は既報のキクタニギク遺伝 子。赤丸はゲノム解読により初 めて推定された遺伝子。
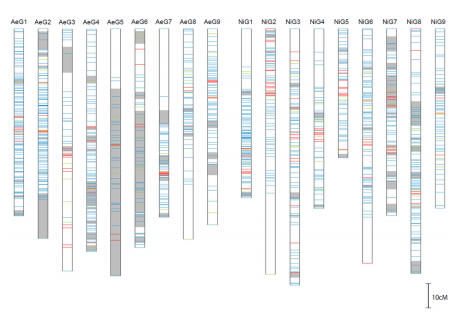
図2:キクタニギクの自 殖可能な系統「AEV2」と 他殖系統「NIFS-0」のゲ ノム配列を比較し、検出 された変異を染色体に沿 ってならべた連鎖地図。 AeG1~AeG9 が「AEV2」の 連鎖地図、NiG1~NiG9 が 「NIFS-0」の連鎖地図。 赤色は変異が多く検出さ れた部位。グレーは対と なる染色体のうち片側の 染色体に偏って後代に遺 伝した部位。自殖可能な 系統「AEV2」では Ae5 と Ae6 で偏りが顕著だった。
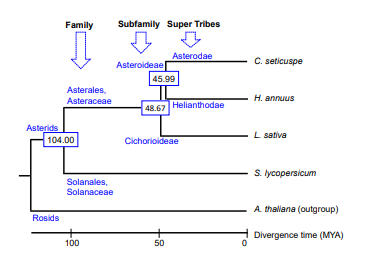
図3:キクタニギク(C. seticuspe:キ ク科キク属)とヒマワリ(H.annus:キ ク科ヒマワリ属)、レタス(L. sativa:キク科アキノノゲシ属)、トマ ト(S. lycopersicum:ナス科ナス 属)、シロイヌナズナ(A. thaliana: アブラナ科シロイヌナズナ属)の分岐の 推定(図内の数字は推定された分岐年 (百万年単位))。およそ 4600 万年前 にキクタニギクとヒマワリが分岐したと 推定される。



