2021-09-14 農研機構,石川県立大学
ポイント
農研機構と石川県立大学は共同で、交配による品種改良において、多くの染色体組み合わせが生じるため優良な個体の選抜が難しいジャガイモやサツマイモなどの高次倍数体1)作物で、迅速にDNAマーカー2)を作製する方法を開発しました。従来は多数の個体ごとに行っていたゲノム3)配列解析を、各作物に適した解析条件を設定し、目的とする性質が異なる2種類の個体群を抽出しそれぞれ混合して解析することで、これまで1年以上かかっていたDNAマーカーの作製期間を最短で2ヶ月に短縮できました。これにより、高次倍数体作物の品種開発において、耐病性やいもの品質など、産地や実需者のニーズの高い性質について、DNAマーカーを用いた選抜作業の効率化が期待されます。
概要
ジャガイモやサツマイモは、それぞれ4組、6組の染色体セットをもつ高次倍数体作物で、交配により得た子孫では非常に多くの染色体組み合わせを生じます。2組の染色体セットをもつ二倍体作物のイネなどと比べると膨大な染色体組み合わせ数となるので、目標とする遺伝子型に近い個体を得ることが難しく、作業に非常に大きな労力が必要です。効率よく個体を選び出すために、病気に強い、いもが美味しいといった性質を選抜できるDNAマーカーを開発して、手間のかかる病気の検定、いもの品質評価を、より簡便なDNAマーカーを用いて苗の段階で行う試みが始まっています。
これまで、いも類でDNAマーカーを作製する場合、交配して得た多数の後代個体について個別にゲノム配列を解析しており、大規模なものとなりがちでした。また、データ解析の工程が多いため、注目する性質を選抜できるDNAマーカーの作製に1年以上かかりました。このため、産地や実需者からの多様なニーズに即応できませんでした。
私たちは解析時間の短縮を目指して、目的とする性質の差異で交配後代を2グループに分けて両者のゲノム配列の違いを解析するQTL-seq法4)に着目しました。ところが、QTL-seq法は、イネなどの二倍体作物向けに開発されたものであったため、染色体セットが2組より多い高次倍数体作物へは適用できませんでした。そこで、複数ある染色体セットごとに有用遺伝子を探索する方法を考案し、4組(ジャガイモ)、および6組(サツマイモ)の染色体セットの数に応じて配列の違いを検出できるように条件を変更することで、高次倍数体作物でDNAマーカーを作製できるpolyploid QTL-seq(ポリプロイドキューティーエルセック)法を開発しました。本方法により、交配後代の性質の調査から最短で2ヶ月でDNAマーカーが効率良く作製できるようになりました。今後、様々な品種改良の場面に適用して有効性の検証を重ね、DNAマーカー開発が大幅に加速化されることにより、産地や実需者のニーズに対して迅速な品種開発が期待できます。
関連情報
予算 : 運営費交付金
問い合わせ先
研究推進責任者 :
農研機構作物研究部門 所長 石本 政男
研究担当者 :
同 作物研究部門 作物デザイン研究領域 上級研究員 山川 博幹
同 九州沖縄農業研究センター 暖地畑作物野菜研究領域 グループ長補佐 田中 勝
同 北海道農業研究センター 寒地畑作研究領域 領域長補佐 兼 グループ長 片山 健二
石川県立大学 生物資源環境学部 准教授 高木 宏樹
広報担当者 :
農研機構作物研究部門 研究推進部 研究推進室 大槻 寛
詳細情報
開発の社会的背景
ジャガイモとサツマイモは、我が国の重要な畑作物で、種いもや苗で増殖する栄養繁殖作物です。生産に重大な影響を及ぼす病害虫に対する抵抗性品種の迅速な開発と産地への普及が望まれています。一方、ジャガイモは野菜として消費される以外にも、ポテトチップスやフライドポテトの原料としても用いられており、サツマイモも従来からあるホクホクとしたものからネットリ濃厚な甘さのものまで多様な食感が好まれるなど、品種開発のニーズが多様化しています。抵抗性の度合いを調べたり、生産物を調理・加工して美味しいものを選んだりする作業はたいへん手間と時間がかかるので、これらの性質と密接に関連するDNAマーカーを作製して、苗の段階でのDNA分析によって選抜し品種育成を省力化する試みが行われています。
ところが、ジャガイモとサツマイモはそれぞれ4組と6組の染色体セットをもつ高次倍数体作物であるため、交配により後代へ受け継がれる染色体の組み合わせが、二倍体作物のイネと比較して非常に多く、極めて多様な後代個体が得られます(図1)。また、染色体セットは、それぞれが互いによく似たDNA配列をもっているため、それらのいずれかのみに存在する有用な遺伝子を見つけ出し、わずかな配列の違いを識別するDNAマーカーを開発することはたいへん難しく、ジャガイモやサツマイモのDNAマーカー開発は遅れていました。
研究の経緯
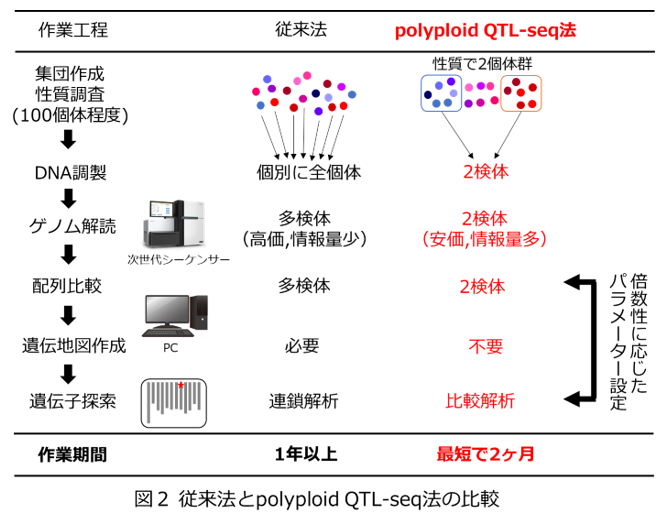
ジャガイモ、サツマイモなどの高次倍数体作物では、有用な遺伝子を探索するため、ある染色体セットと他とを識別できるDNA配列の違いに着目し、後代個体への受け継がれ方を調べます。従来は、染色体上の任意の箇所を選んでDNA配列の違いを探索し、有用な遺伝子との関連があるDNA配列の違いを探す作業を繰り返していました。その後、次世代シーケンサー5)を活用した技術が普及し、交配で得られる後代から多数の個体について調査箇所を増やして解析できるようになりました。その過程では、多数のDNA分析試料の調製、ゲノム配列データの相互比較、遺伝地図6)の作成、注目する遺伝子の探索などの多くの工程を、それぞれの専門家が手分けして、進捗状況に応じて相互に連絡調整しながら作業を進めるため、1つのDNAマーカーの作製に1年以上かかり、産地や実需者からの多様な品種開発ニーズに即応した迅速なDNAマーカー開発が困難でした(図2)。
一方、少ない分析検体数でDNAマーカーを作製できる方法としてQTL-seq法があります。この方法では、後代個体を目的の性質を受け継ぐ個体と受け継がない個体の2グループに分けてゲノム配列を解読し、グループ間で配列が異なる箇所を探します。わずか2検体のゲノム配列の解読で済み、解読した配列データからDNAマーカー候補の提示までを少数の研究者が一貫して行うため、DNAマーカー開発に要する期間を大幅に短縮できます。しかし、この方法はイネなどの二倍体作物向けに開発されたものであるため、2組を超える多数の染色体セットが混在する状況での配列の検出には対応できず、そのままではジャガイモやサツマイモに適用できませんでした。そこで、私たちはQTL-seq法を高次倍数体作物にも適用できるように改良を試み、ジャガイモやサツマイモのDNAマーカー開発の迅速化を目指しました。
研究の内容・意義
1.高性能次世代シーケンサーを活用した染色体セットの識別
有用遺伝子の探索を高い精度で行うためには、まず、ジャガイモで4組、サツマイモで6組の染色体セットを相互に識別することが必要です。そこで、染色体セットのいずれかのみに存在するDNA配列を特定するため、全ゲノム配列量の50倍に相当する大量の解読データを取得しました。次世代シーケンサーの性能が大幅に向上し、ゲノムの全領域を対象に充分な量の解読データが安価に得られるようになったため、取りこぼしのない詳細な識別が可能となりました。
2.倍数性程度に応じた解析パラメーターの設定
よく似た配列をもつ染色体セットが複数あるなかで、目的とする有用遺伝子だけを効率よく検出できる解析パラメーターを設定しました。染色体セットの数が増加するほど、真の目的遺伝子に対して、類似の遺伝子の割合が増加するため、染色体セットを4組もつジャガイモは目的遺伝子が検出されにくくなり、6組もつサツマイモでは、さらに検出が難しくなります。そこで、予想される検出頻度に応じて検出条件を調整することで、それぞれの倍数性ごとに最適な解析パラメーターを明らかにしました。これにより、様々な染色体セット数の高次倍数体作物に対応できるようになったことから、本方法を高次倍数体作物向けのQTL-seq法としてpolyploid QTL-seq法と命名しました(図2)。
3.ジャガイモとサツマイモでのDNAマーカー迅速作製の実証
既知のジャガイモにおけるジャガイモシストセンチュウ抵抗性遺伝子、サツマイモにおけるいも内部への紫色素(アントシアニン色素)の蓄積遺伝子について、polyploid QTL-seq法を適用し、有効性を確認しました。その結果、それぞれの特性を決定する遺伝子を5番染色体および12番染色体に検出でき、センチュウ抵抗性やいもの色を正確に判別できるDNAマーカーを後代個体の調査からそれぞれ3ヶ月および2ヶ月で作製できました。本手法の特長として、近縁の品種同士を含めた幅広い交配組合せに適用しやすく、発表論文に記載された通りに実施すれば、試料調製からDNAマーカー作製までを研究者が短期間で行うことができることがあげられ、様々な品種改良の場面において利用できます。
今後の予定・期待
今後は、関与する遺伝子が多数となる難易度が高いものへの対策技術を開発するとともに、病虫害抵抗性やいもの品質など、ジャガイモやサツマイモなどの品種開発における重要な性質についてDNAマーカーを作製し、産地や実需者のニーズにあった品種の迅速な開発に役立てていく予定です。
また、本方法は、ゲノム配列が解読されている高次倍数体作物であれば、いずれにも適用可能であるため、サトウキビ、キク、バラ等の他の高次倍数体作物のDNAマーカー育種への貢献も期待できます。
用語の解説
- 1)高次倍数体:
- イネ、ダイズなど多くの作物は、生存に必要な染色体のセットを2組もつため、二倍体といわれます。これに対して、生存に必要な染色体セットを2組より多くもつ作物には、ジャガイモ(4組)、サツマイモ(6組)、コムギ(6組)などがあり、これらは高次倍数体作物と総称されます。高次倍数体は、二倍体に比べて植物体が大きくなるなど、農業で役立つ性質を示すことから、栽培種として利用されています。染色体のセット数が増えるごとに子孫に見られる染色体の組み合わせの種類が増えるため、選抜したい遺伝子組み合わせを持つ個体の出現確率が非常に低くなる場合が多く、品種改良は難しくなります。
- 2)DNAマーカー:
- 品種間でのDNA配列の違いを検出する標識のこと。品種開発では、既存の品種に、病気に強い、実が美味しいといった、有用な性質を付与することで、新しい品種が開発されます。病気の検定や収穫物の食味の調査は非常に手間がかかるので、これらの有用な性質の有無を判別できるDNAマーカーをつくることで、畑に植え付ける前の苗の段階で、有用な性質をもつ個体を選ぶことができるため、品種開発の効率化に役立ちます。
- 3)ゲノム:
- 生物の形態を決め、その生存に必要な最小限の染色体セット、またはDNA全体のことをいいます。
- 4)QTL-seq法:
- 病気に対する強さの度合いや収穫量など、量的な性質を決める遺伝子の位置(量的形質遺伝子座、QTLともいいます)を特定する方法のひとつ。評価値の大きい個体グループと小さいグループに分けて、グループごとにひとまとめにして次世代シーケンサーでゲノム配列を解読し、配列の違いがある箇所を特定することで、簡便かつ迅速にQTLを検出します。近年、イネ、ダイズなどの様々な二倍体作物種で用いられ、DNAマーカーが開発されています。
- 5)次世代シーケンサー:
- 供試した生物種のゲノム全体など、一度に大量のDNA配列を解読できるDNAシーケンサーの総称。近年、安価に1,000億塩基以上もの配列データを取得可能となっています。
- 6)遺伝地図:
- 遺伝子やDNAマーカーの染色体上の位置を示した地図のこと。各遺伝子の後代への受け継がれ方に基づいて作成されます。
発表論文
Hiromoto Yamakawa, Emdadul Haque, Masaru Tanaka, Hiroki Takagi, Kenji Asano, Etsuo Shimosaka, Kotaro Akai, Satoshi Okamoto, Kenji Katayama, Seiji Tamiya (2021) Polyploid QTL-seq towards rapid development of tightly linked DNA markers for potato and sweetpotato breeding through whole-genome resequencing. Plant Biotechnol. J.
URL: https://doi.org/10.1111/pbi.13633
参考図